一種鑑別6種紫檀屬木材的DNA組合條形碼及其鑑別方法和應用與流程
2023-05-03 01:32:56 4
本發明屬於木材材種鑑定的分子生物學檢測領域,具體涉及一種鑑別6種紫檀屬木材的dna組合條形碼及其鑑別方法和應用。
背景技術:
紫檀屬(pterocarpusjacq.)隸屬豆科(leguminosae),約70種,主要分布於熱帶及亞熱帶地區。紫檀屬木材以其木材品質及藥用價值聞名全球。由於巨大經濟利益鏈的存在和社會對其需求量的不斷增加,非法及過度開採使紫檀屬木材資源日益匱乏。因此,紫檀屬木材資源逐漸得到了國際法律法規的關注。目前,檀香紫檀和刺蝟紫檀2個樹種被列入瀕危野生動植物種國際貿易保護公約(cites)附錄ii;數個紫檀屬樹種也被列入國際自然保護聯盟(iucn)紅色名錄;同時,印度紫檀於1999年被中國政府列入國家重點保護野生植物名錄。
紫檀屬木材樹種識別為保護木材資源及法律法規的實施提供了技術支持。然而,基於木材解剖學的傳統識別技術只能鑑別紫檀屬木材到「屬」或者「類」,無法實現「種」水平的鑑別。而新興的dna條形碼技術為紫檀屬木材「種」水平識別提供了可能。
dna條形碼是一段標準的、具有足夠變異的、易擴增且相對較短的dna片段。近年來,dna條形碼已經發展成為物種鑑定的重要工具。但單一dna條形碼對於物種尤其針對進化關係複雜物種的識別能力較為有限。而dna組合條形碼通過多條單一序列的組合具有更豐富的序列信息位點,進而提高物種識別能力,是一種有效的物種鑑別方法。
總體來說,紫檀屬木材物種豐富,基於木材解剖學的傳統識別技術難以實現木材「種」水平的識別,而新興的dna條形碼技術,特別是dna組合條形碼逐步發展成為木材識別的有效工具。
技術實現要素:
本發明要解決的技術問題是針對傳統木材識別技術無法準確鑑別6種紫檀屬木材。
所以,本發明的第一目的是提供一種鑑別6種紫檀屬木材的dna組合條形碼。
本發明的第二目的是提供一種鑑別6種紫檀屬木材的方法。
本發明的第三目的是提供所述dna組合條形碼和分子生物學方法在鑑別6種紫檀屬木材中的應用。
基於此,本發明的技術方案如下:
本發明首先提供了一種鑑別6種紫檀屬木材的dna組合條形碼,所述dna組合條形碼是條形碼序列matk、ndhf-rpl32、rbcl或its2中的任意2種以上或全部組合形成的dna組合條形碼。
優選的,所述dna組合條形碼是matk+ndhf-rpl32+its2組合條形碼。該dna組合條形碼為細胞核基因its2序列與質體基因(matk和ndhf-rpl32)組合。所述matk+ndhf-rpl32+its2序列如seqidno.9-14所示。
優選的,所述6種紫檀屬木材分別為安哥拉紫檀pterocarpusangolensisdc.、印度紫檀pterocarpusindicuswilld.、大果紫檀pterocarpusmacrocarpuskurz、檀香紫檀pterocarpussantalinusl.f.、非洲紫檀pterocarpussoyauxiitaub.及染料紫檀pterocarpustinctoriuswelw.。
進一步地,本發明提供了一種鑑別6種紫檀屬木材的方法,該方法利用dna組合條形碼,並通過分子生物學手段來鑑別6種紫檀屬木材;所述dna組合條形碼是條形碼序列matk、ndhf-rpl32、rbcl或its2中的任意2種以上或全部組合形成的dna組合條形碼。
具體地,所述方法包括以下步驟:
(1)將木材樣品研磨處理成木粉;
(2)提取步驟(1)所得的木粉樣品的dna;
(3)以步驟(2)提取得到的dna為模板,pcr擴增所述matk、ndhf-rpl32和its2條形碼序列;
(4)將步驟(3)得到的pcr擴增產物進行測序,得到matk、ndhf-rpl32和its2序列,並對其進行組合;
(5)以步驟(4)所得的matk+ndhf-rpl32+its2條形碼組合基於taxondna法和系統發育進化樹法鑑別6種紫檀屬木材。
優選的,步驟(1)所述的木粉研磨至200目及以上。
優選的,步驟(2)中所述dna需進行純化,dna終濃度為1-200ng/μl。
優選的,步驟(3)所述pcr擴增的matk引物序列如seqidno.1-2所示,ndhf-rpl32引物序列如seqidno.3-4所示,its2引物序列如seqidno.5-6所示。
優選的,步驟(3)所述pcr擴增反應體系為0.5-3udna聚合酶、1.0-2.0mmmgcl2、200μm單一dntp、0.1-5.0μm單一引物、ph7.0-8.0的0.1-1.5mg/ml牛血清白蛋白和10-1000ng模板dna;pcr反應條件為94-96℃預變性0.5-10min;94-96℃變性0.05-2min,40-65℃退火0.5-2min,72℃延伸0.3-2min,循環20-50次;72℃終延伸2-15min。
優選的,步驟(5)中taxondna法基於「bestmatch」和「bestclosematch」2個指標判別;系統發育進化樹法基於鄰接法鑑別。
更進一步地,本發明提供了上述dna組合條形碼,或上述鑑別6種紫檀屬木材的方法在紫檀屬木材鑑別中的應用。
本發明具有如下優點:
1、本發明基於一種dna組合條形碼,可以實現6種紫檀屬木材的準確鑑別,突破了傳統木材識別技術無法識別木材到「種」的局限;
2、本發明篩選的鑑別引物特異性好,擴增及測序成功率較高;
3、本發明優選的matk+ndhf-rpl32+its2序列組合dna條形碼在紫檀屬6種木材中存在明顯的差異位點,具有很強的鑑別能力;
4、本發明優選的taxondna法和系統發育進化樹法操作簡單,且基於這兩種方法綜合區分樹種,識別準確度高;
5、本發明取樣量極少,且不受取材位置(邊材、心邊材過渡區及心材)、樣品原始狀態(木塊、木粉)因素影響;
6、本發明實驗條件依賴少,一般pcr實驗室均可滿足;
7、本發明為紫檀屬木材的準確識別提供了一種新的途徑和思路。
總之,本發明提供的dna組合條形碼及其方法可以實現6種紫檀屬木材的準確鑑別,解決了傳統木材識別方法無法鑑別紫檀屬木材到「種」水平的難題,為海關、質量檢驗檢疫等木材貿易執法部門和木材經營貿易人員提供一種高效可靠的鑑別方法,具有較高的實用價值。
附圖說明
圖1基於taxondna法的「bestmatch」(a)和「bestclosematch」(b)的單一及組合條形碼的物種識別成功率;
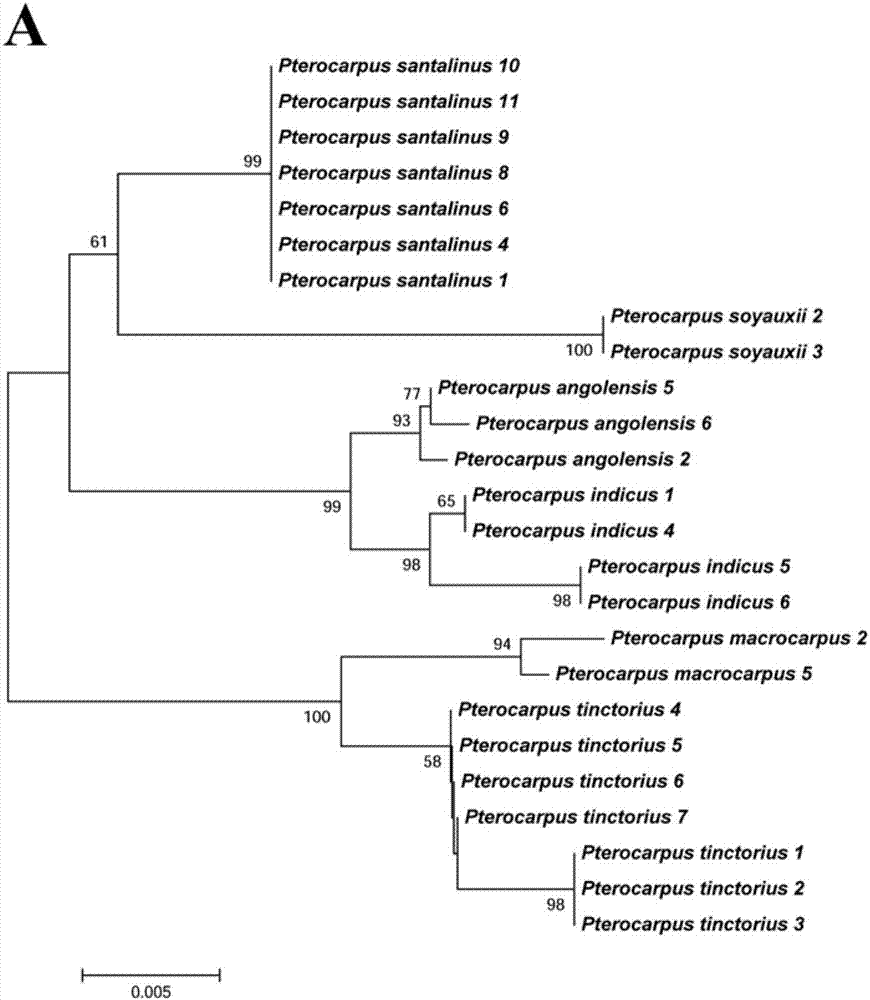
圖2基於dna組合條形碼構建的系統發育鄰接樹(a)matk+ndhf-rpl32+its2,(b)matk+rbcl+its2;
圖3基於dna組合條形碼matk+ndhf-rpl32+its2鑑別未知樣品的系統發育鄰接樹。
具體實施方式
以下實施例僅用於說明本發明,但不用來限制本發明的發明範圍。該技術領域的技術工程師可根據上述發明的內容做出一些非本質性的改進和調整。
實施例1:紫檀屬樹種木材特異性引物設計
(1)從genbank中下載紫檀屬的質體dna序列matk、ndhf-rpl32、rbcl和細胞核dna序列its2(表1);
表1genbank中下載的紫檀屬dna條形碼序列
(2)應用clustalx1.81軟體比對序列,並查找確定紫檀屬間4種dna條形碼序列的差異位點;
(3)應用primerpremier5軟體對matk、ndhf-rpl32、rbcl和its2四個條形碼設計引物。所述擴增引物如表2所示。
表2四種dna條形碼引物信息
實施例2:6種紫檀屬木材標準樣品的dna組合條形碼優選與確定
(1)標準樣品採集。
6種紫檀屬標準樣品(分別為安哥拉紫檀、印度紫檀、大果紫檀、檀香紫檀、非洲紫檀及染料紫檀)合計39號,均取自中國林業科學研究院木材標本館。
(2)樣品製備。
選取木材樣品,利用70%酒精消毒後的解剖刀片將木材試樣外表面切除,以避免外源汙染;將木材試樣切成若干木屑,並置於低溫冷凍研磨儀中低溫預冷3min,研磨3min,運行頻率10cps;研磨結束後,過200目篩網,將細木粉分裝到若干50ml的微量離心管中,每管木粉量500mg,並置於-80℃低溫冰箱保存備用。
(3)dna提取。
在消毒處理的超淨工作環境中,參照參考文獻jiao等文章(jiaol,yiny,chengy,jiangx.dnabarcodingforidentificationoftheendangeredspeciesaquilariasinensis:comparisonofdatafromheatedoragedwoodsamples.holzforschung.2014;68(4):487-494.)對6種紫檀屬木材進行dna提取。
(4)pcr擴增反應與測序。
引物對為實施例1中的四種dna條形碼序列引物對,以dna提取物為模板進行pcr擴增,反應體系為30μl:其中premixextaq15μl(包括l.25uextaqdna聚合酶,2mmmgcl2,200μm單一dntp),0.2μm單一引物和約20ng模板dna。所有pcr反應均在pcr擴增儀上進行。
反應程序為:94℃預變性2min;94℃變性15s,52℃(matk)、47℃(ndhf-rpl32)、50℃(rbcl)及51℃(its2)退火30s,72℃延伸20s,循環40次;72℃終延伸7min,即可獲得高效擴增的dna目的片段。將擴增產物純化後進行雙向直接測序。
(5)序列比對分析與序列組合。
應用contigexpress軟體對測序結果進行測序質量評估,去除兩端低質量部分,並對剩餘部分進行質量評估,如果滿足質量要求,方可用於序列拼接及校對。6種紫檀屬木材的matk、ndhf-rpl32、rbcl及its2四種條形碼序列genbank登錄號和序列特徵信息分別如表3和表4所示。
應用editseq軟體分別對6種紫檀屬木材物種的四種條形碼進行組合,得到matk+its2、matk+ndhf-rpl32、matk+rbcl、ndhf-rpl32+its2、ndhf-rpl32+rbcl、rbcl+its2、matk+ndhf-rpl32+its2、matk+ndhf-rpl32+rbcl、matk+rbcl+its2、ndhf-rpl32+rbcl+its2、matk+ndhf-rpl32+rbcl+its2等11個dna條形碼組合。
表3本研究測序得到的6種紫檀屬木材的四種條形碼序列genbank登錄號
表4四種dna條形碼序列特徵信息
(6)序列組合dna條形碼優選與確定。
應用mega軟體通過k2p距離模型對單一及dna組合條形碼的種內距離和種間距離進行計算分析,具體如表5所示。
利用taxondna軟體中「bestmatch」和「bestclosematch」2個指標鑑別樹種,結果表明,matk+its2和matk+ndhf-rpl32+its2能夠識別以上6種紫檀屬木材樹種(圖1);應用mega軟體基於鄰接法構建系統發育樹,matk+ndhf-rpl32+its2和matk+rbcl+its2對6種紫檀屬木材有100%的物種識別成功率(圖2)。
綜合利用taxondna法與系統進化樹法兩種方法,對單一條形碼及11個條形碼組合進行篩選,確定識別6種紫檀屬木材的最優dna組合條形碼為matk+ndhf-rpl32+its2(seqidno.9-14)。
表5單一及dna組合條形碼的種內及種間距離
實施例3:未知木材樣品dna鑑別
(1)1塊木材樣品取自木材市場,通過對其進行解剖構造鑑定,鑑定為紫檀木類木材,但無法判定到檀香紫檀樹種。因此基於dna方法鑑別木材。
(2)製備木粉並研磨至200目及以上。
(3)木材dna提取。
在消毒處理的超淨工作環境中,參照實施例2中的dna提取方法,對木材進行dna提取。所述dna還需進行純化,dna終濃度為1-200ng/μl。
(4)pcr擴增反應與測序。
木材dna提取物為模板進行pcr擴增,擴增引物如seqid1-6所示。反應體系為30μl:其中premixextaq15μl(包括l.25uextaqdna聚合酶,2mmmgcl2,200μm單一dntp),0.2μm單一引物和約20ng模板dna。所有pcr反應均在pcr擴增儀上進行。反應程序為:94℃預變性2min;94℃變性15s,52℃(matk)、47℃(ndhf-rpl32)及51℃(its2)分別退火30s,72℃延伸20s,循環40次;72℃終延伸7min,即可獲得高效擴增的dna目的片段。將擴增產物純化後進行雙向直接測序。
(5)序列比對分析與樹種鑑別。
對matk、ndhf-rpl32及its2三個序列的測序結果進行組合,採用組合序列matk+ndhf-rpl32+its2構建系統發育進化樹,如圖3所示。分析結果表明該樣品能夠與檀香紫檀樣品聚類,而與其他紫檀屬樹種區分開。聚類結果證明該樣品為檀香紫檀。
雖然,上文中已經用一般性說明及具體實施方案對本發明作了詳盡的描述,但在本發明基礎上,可以對之作一些修改或改進,這對本領域技術人員而言是顯而易見的。因此,在不偏離本發明精神的基礎上所做的這些修改或改進,均屬於本發明要求保護的範圍。
sequencelisting
中國林科院木材工業研究所
一種鑑別6種紫檀屬木材的dna組合條形碼及其鑑別方法和應用
011701703
14
patentinversion3.5
1
24
dna
人工序列
1
tttcgtctaccttatccttcttca24
2
22
dna
人工序列
2
ctagcatttgactccgtaccac22
3
22
dna
人工序列
3
gattcgtaatgagttttgtttc22
4
20
dna
人工序列
4
aggaatttgtttattggacc20
5
18
dna
人工序列
5
atgcgatacttggtgtga18
6
18
dna
人工序列
6
tagccccgcctgacctga18
7
18
dna
人工序列
7
tgccgaatcttctactgg18
8
17
dna
人工序列
8
ataagaaacggtccctc17
9
743
dna
安哥拉紫檀組合序列
9
tttcgtctaccttatccttcttcaaggatcctttgattcattatgttagatatcaaggaa60
aatccattctggcttcaaagaatgcgcctcttttgatgaataaatggaaatactatctca120
tctatttctggcaatgtcattttgatgtttggtctcaaccaggaacgatccatataaacc180
aattattatccgagcattcatttaactttttttgggggggctgtctttcaaatgtgcggt240
tcgtaatgagttttgtttcttattcgtcggttttatctcttttgtaaaggcttcagttaa300
taaaaaagagtgaacatataaatagaattttctattattctgaatctctgcacaatactt360
ctaatattgcaaagtacaaagtaaaaatggtccaataaacaaattcgtgtgaattgcaga420
atcccgtgaaccatcgagtctttgaacgcaagttgcgcccaaagccattaggctaagggc480
acgcctgcctgggtgtcacaaatcgttgccccaatccccgcgcctgtaggcgccgggcgg540
cggggcgaatgctggcttcccgtgagcgagcgcctcgcggttggccgaaaatcgggttcg600
tggtggagggcagcgccatgacagacggtggttgagtgcagtctcgaggccagtcgtgcg660
cggtcccctccgctagtcacggactccgtgacccaacaacggcatcgatcgcccatgatg720
cgacctcaggtcaggcggggcta743
10
743
dna
印度紫檀組合序列
10
tttcgtctaccttatccttcttcaaggatcctttgattcattatgttagatatcaaggaa60
aatccattctggcttcaaagtatgcccctctttcgatgaataaatggaaatactatctca120
tctatttctggcaatgtcattttgatgtttggtctcaaccaggaacgatccatataaacc180
aattattatccgagcattcatttaactttttttgggggggttatctttcaaatgtgcggt240
tcgtaatgagttttgtttcttattcgtcggttttatctcttttgtaaaggcttcagttaa300
taaaaaagagtgaacatataaatagaattttctattattctgaatctctgcacaatactt360
ctaatattgcaaagtacaaagtaaaaatggtccaataaacaaattcgtgtgaattgcaga420
atcccgtgaaccatcgagtctttgaacgcaagttgcgcccaaagccattaggctaagggc480
acgcctgcctgggtgtcacaaatcgttgccccaatccccgcgcctgtaggcgccgggcgg540
cggggcgaatgctggcttcccgcgagcgagcgcctcgcggttggccgaaaatcgggctcg600
tggtggagggcagcgccatgacagacggtggttgagtgcaatctcgaggccagtcgtgcg660
cggtcccctccgctagtcatggactccgtgacccaacaacggcatcgatcgcccatgatg720
cgacctcaggtcaggcggggcta743
11
749
dna
大果紫檀組合序列
11
tttcgtctaccttatccttcttcaaggatcctttgattcattatgttagatatcaaggaa60
aatccattctggcttcaaagaatgcccctctttcgatgaataaatggaaatactatctca120
tctatttctggcaatgtcattttgatgtttggtctcaaccaggaacgatccatataaacc180
aattattatccgagcattcatttaactttttttgggggggttatctttcaaatgtgcggt240
tcgtaatgagttttgtttcttattcgtcggttttatctcttttgtaaaggcttcagttaa300
taaaaaagagtgaacatataaatagaattttctattattctgaatctctgcacaatactt360
ctaatattgcaaagtacaaagtcaaaatggtccaataaacaaattcgtgtgaattgcaga420
atcccgtgaaccatcgagtctttgaacgcaagttgcgcccgaagccattaggctaagggc480
acgcctgcctgggtgtcaccaatcgttgccccaaccccagcgcctctactctagggcact540
gggtgggaggggtgaatgctggcttcccgtgagcgagtgcctcacggttggctgaaaatc600
gggttcgtggtggagggtagcgccatgacagacggtggttgagtgcaatctcgaggccag660
tcgtgcacgtcccctccgccggttacgaactccgtgacccgtgagcggcaccgatcgccc720
atgatgcgacctcaggtcaggcggggcta749
12
749
dna
檀香紫檀組合序列
12
tttcgtctaccttatccttcttcaaggatcctttgattcattatgttagatatcaaggaa60
aatccattctggcttcaaagaatgcgcctctttcgatgaataaatggaaatactatctca120
tctatttctggcaatgtcattttgatgtttggtctcaaccaggaacgatccatataaacc180
aattattatccgagcattcatttaactttttttgggggggttatctttcaaatgtgcggt240
tcgtaatgagttttgtttcttattcgtcggttttatctcttttgtaaaggcttcagttaa300
taaaaaagagtgaacatataaatagaattttctattattctgaatctctgcacaatactt360
ctaatattgcaaagtacaaagttaaaatggtccaataaacaaattcgtgtgaattgcaga420
atcccgtgaaccatcgagtctttgaacgcaagttgcgcccgaagccattaggctaagggc480
acgcctgcctgggtgtcacaaatcgttgccccaatccccgcgccgctcctgtgggcgccg540
ggctgcggggcgaatgctggcttcccgtgagcgagtgcctcgcggttggccgaaaatcgg600
gttcgtggtggagggtaagcgccatgacagacggtggttgagcgcaatctcgaggccagt660
cgtgcgcggtcccctccgctagttacggactccgtgacccgtgagcggcaccgatcgccc720
atgatgcgacctcaggtcaggcggggcta749
13
748
dna
非洲紫檀組合序列
13
tttcgtctaccttatccttcttcaaggatcctttgattcattatgttagatatcaaggaa60
aatccattctggcttcaaagaatgcgcctcttttgatgaataaatggaaatactatctca120
tctatttctggcaatgtcattttgatgtttggtctcaaccaggaacgatccatataaacc180
aattattatccgagcattcatttaactttttttgggggggctatctttcaaatgtgcggt240
tcgtaatgagttttgtttcttattcgtcggttttatctcttttgtaaaggcttcagttaa300
taaaaaagagtgaacatataaatagaattttctattattctgaatctctgcacaatactt360
ctaatattgcaaagtacaaagttaaaatggtccaataaacaaattcgtgtgaattgcaga420
atcccgtgaaccatcgagtctttgaacgcaagttgcgcccgaagccattaggctaagggc480
acgcctgcctgggtgtcacaaatcgttgccccaatcaatcccggcgcctaataaaggcgc540
tgggcggggcgaatgctggcttcccgtgagcgagtgcctcgcggctggccgaaaatcggg600
tccgtggtggagggcagcgccatgacagacggtggttgagcgcaatctcgaggccagtcg660
tgcgcggtcccctctgctagctacggactccgtgacccgtggagcggcaccgatcgccca720
tgatgcgacctcaggtcaggcggggcta748
14
751
dna
染料紫檀組合序列
14
tttcgtctaccttatccttcttcaaggatcctttgattcattatgttagatatcaaggaa60
aatccattctggcttcaaagaatgcgcctcttttgatgaataaatggaaatactatctca120
tctatttctggcaatgtcattttgatgtttggtctcaaccaggaacgatccatataaacc180
aattattatccgagcattcatttaactttttttgggggggctatctttcaaatgtgcggt240
tcgtaatgagttttgtttcttattcgtcggttttatctcttttgtaaagtcttcagttaa300
taataataaaaaagagtgaacatataaatagaattttctattattctgaatctctgcaca360
atacttctaatattgcaaagtacaaagtaaaaatggtccaataaacaaattcgtgtgaat420
tgcagaatcccgtgaaccatcgagtctttgaacgcaagttgcgcccgaagccattaggct480
gagggcacgcctgcctgggtgtcaccaatcgttgccccaaccccagcgcctctactctag540
ggcactgggcggggtgaatgctggcttcccgtgagcgagtgcctcgcggttggccgaaaa600
tcgggttcgtggtggagggtagcgccatgacagacggtggttgagtgcaatctcgaggcc660
agtcgtgcgcgtcccctccgccggttacggactccgtgacccgtgagcggcaccgatcgc720
ccatgatgcgacctcaggtcaggcggggcta751